[←][→] ath
| functional annotation | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Function | mitochondrial lipoamide dehydrogenase 1 |




|
||||||||||||||||||||||||||||||||||||||||||||||||
| GO BP |
|
|||||||||||||||||||||||||||||||||||||||||||||||||
| GO CC |
|
|||||||||||||||||||||||||||||||||||||||||||||||||
| GO MF |
|
|||||||||||||||||||||||||||||||||||||||||||||||||
| KEGG | ath00010 [list] [network] Glycolysis / Gluconeogenesis (119 genes) |  |
||||||||||||||||||||||||||||||||||||||||||||||||
| ath00020 [list] [network] Citrate cycle (TCA cycle) (64 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00260 [list] [network] Glycine, serine and threonine metabolism (70 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00280 [list] [network] Valine, leucine and isoleucine degradation (52 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00310 [list] [network] Lysine degradation (31 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00380 [list] [network] Tryptophan metabolism (64 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00620 [list] [network] Pyruvate metabolism (97 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00630 [list] [network] Glyoxylate and dicarboxylate metabolism (78 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath00640 [list] [network] Propanoate metabolism (41 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath01200 [list] [network] Carbon metabolism (273 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| ath01240 [list] [network] Biosynthesis of cofactors (236 genes) |  |
|||||||||||||||||||||||||||||||||||||||||||||||||
| Protein | NP_001322047.1 NP_001322048.1 NP_001322049.1 NP_175237.1 NP_849782.1 | |||||||||||||||||||||||||||||||||||||||||||||||||
| BLAST | NP_001322047.1 NP_001322048.1 NP_001322049.1 NP_175237.1 NP_849782.1 | |||||||||||||||||||||||||||||||||||||||||||||||||
| Orthologous | [Ortholog page] LOC544237 (sly) LOC547523 (gma) FLBR (gma) mtLPD2 (ath) LOC4326980 (osa) LOC4337881 (osa) LOC7471086 (ppo) LOC7485860 (ppo) LOC25494137 (mtr) LOC100788043 (gma) LOC101245444 (sly) LOC103869701 (bra) LOC103871503 (bra) LOC123038886 (tae) LOC123108104 (tae) LOC123114079 (tae) LOC123180227 (tae) LOC123180603 (tae) LOC123189229 (tae) LOC123409249 (hvu) LOC123426241 (hvu) | |||||||||||||||||||||||||||||||||||||||||||||||||
| Subcellular localization wolf |
|
|||||||||||||||||||||||||||||||||||||||||||||||||
| Subcellular localization TargetP |
|
|||||||||||||||||||||||||||||||||||||||||||||||||
| Gene coexpression | ||||||||||||||||||||||||||||||||||||||||||||||||||
| Network*for coexpressed genes |
|
|||||||||||||||||||||||||||||||||||||||||||||||||
|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|---|
| Coexpressed gene list |
[Coexpressed gene list for mtLPD1] | |||||||||||||||||||||||||||||||||||||||||||||||||
| Gene expression | ||||||||||||||||||||||||||||||||||||||||||||||||||
| All samples | [Expression pattern for all samples] | |||||||||||||||||||||||||||||||||||||||||||||||||
| AtGenExpress* (Development) |
260730_at
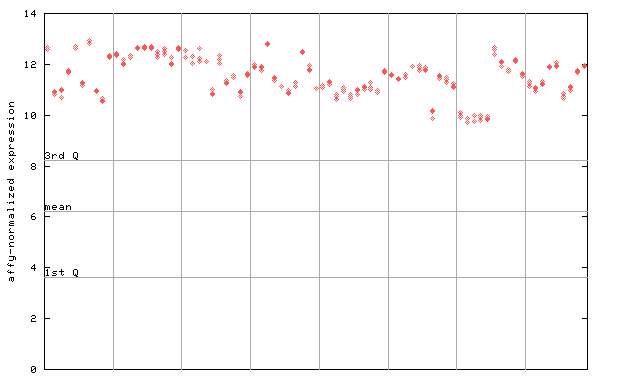
X axis is samples (pdf file), and Y axis is log2-expression. |
|||||||||||||||||||||||||||||||||||||||||||||||||
| AtGenExpress* (Stress) |
260730_at
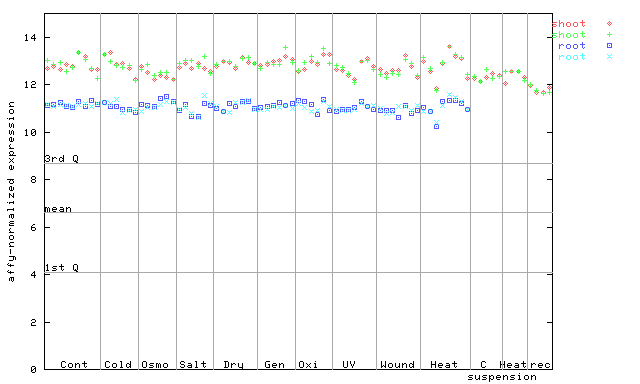
X axis is samples (pdf file), and Y axis is log2-expression. |
|||||||||||||||||||||||||||||||||||||||||||||||||
| AtGenExpress* (Hormone) |
260730_at
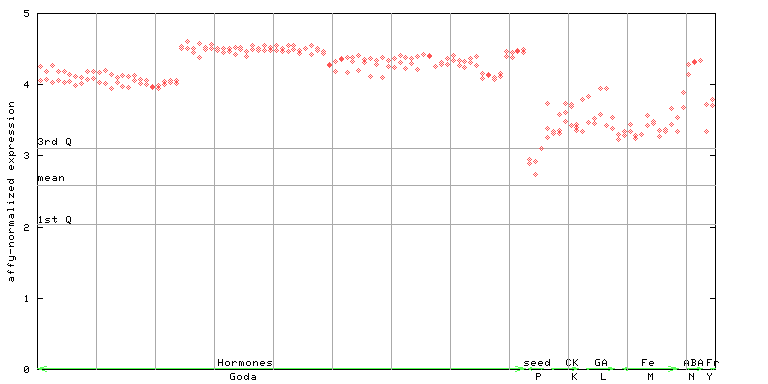
X axis is samples (xls file), and Y axis is log-expression. |
|||||||||||||||||||||||||||||||||||||||||||||||||
| Link to other DBs | ||
| Entrez Gene ID | 841221 |


|
| Refseq ID (protein) | NP_001322047.1 |  |
| NP_001322048.1 |  |
|
| NP_001322049.1 |  |
|
| NP_175237.1 |  |
|
| NP_849782.1 |  |
|
The preparation time of this page was 0.1 [sec].






